Haplogrupo A
A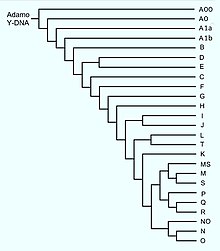
| Fecha original | 140.000 antes del presente, 270.000 antes del presente o 275.000 antes del presente |
|---|---|
| Lugar de origen | África central |
| Antepasado | Cromosómico Adam-Y |
| Descendientes | A00, A0, A1a, A1b |
| Frecuencias más altas |
Namibia ( San Tsumkwe, Nama ) 60-70% Sudán del Sur ( Dinka , Shilluk , Nuer ) 33% -61,5% |
En genética humana , haplogrupo A (M91) es un haplogrupo del cromosoma Y . El haplogrupo A, que se origina y es más diverso en África, es también el más antiguo de los haplogrupos. Se refiere a un grupo de linajes del cromosoma Y que fue la primera rama que se originó en la raíz de la filogenia del cromosoma Y de los humanos modernos . Las mutaciones que definen al haplogrupo A habrían llegado a los cromosomas Y de algunos de los primeros descendientes del cromosoma Adán , incluido al menos uno de sus hijos. Tenga en cuenta que una variante arcaica traída por la hibridación define un haplogrupo distinto llamado A00.
El haplogrupo A está prácticamente concentrado en partes de África , aunque se han notificado algunos casos en Asia occidental . Este clado obtiene sus mayores frecuencias actualmente en la población san de cazadores-recolectores del sur de África , seguida de cerca por muchos grupos del Nilo en el este de África . Sin embargo, los subclades más antiguos del haplogrupo A se encuentran exclusivamente en África Central . En 2011, Fulvio Cruciani et al. calculado por la diversidad del ADN del cromosoma Y como el cromosoma Y Adam se remonta aproximadamente a 140.000 años. Este clado también se ha observado con frecuencias notables en algunas poblaciones de Etiopía y en algunos grupos pigmeos de África Central.
El haplogrupo A es menos común entre los hablantes de lenguas niger-congoleñas , que en su mayoría pertenecen al clado E1b1a . Generalmente se cree que el haplogrupo E se originó en el noreste de África y luego entró en África occidental, desde donde se extendió hace 5.000 años a África central, luego desde el sur y el sureste con la expansión bantú . Según Wood et al. (2005) y Rosa et al. (2007), estos movimientos de población relativamente recientes de África occidental cambiaron la diversidad del cromosoma Y preexistente en las poblaciones de África central, meridional y sudoriental, reemplazando los haplogrupos anteriores en estas regiones por los ahora dominantes linajes E1b1a. Sin embargo, hoy en día, se pueden observar vestigios de los habitantes ancestrales de estas regiones por la presencia de los haplogrupos YDNA A-M91 y B-M60 que son comunes en ciertas poblaciones relictas, como los pigmeos Mbuti del bosque de Ituri (en el República Democrática del Congo ) y el Khoisan del sur de África .
Histórico
La primera secuenciación del cromosoma Y humano sugirió que la primera bifurcación en el árbol genealógico del cromosoma Y ocurrió con la mutación M91 que separa al haplogrupo A del haplogrupo BT . Sin embargo, ahora se reconoce que la bifurcación más antigua del árbol del cromosoma Y se encuentra entre dos subclades ya descritos del haplogrupo A, en lugar de entre el haplogrupo A y el haplogrupo BT (grupo ancestral del conjunto de haplogrupos de B a T). Los subclades A1b y A1a-T ahora descienden directamente de la raíz del árbol. Este reordenamiento del árbol genealógico del cromosoma Y lleva a considerar que las líneas clasificadas en el haplogrupo A no forman necesariamente un clado monofilético . Entonces, el haplogrupo A se refiere primero a un conjunto de líneas que no tienen los marcadores genéticos que definen al haplogrupo BT (y sus derivados), aunque muchas líneas incluidas en el haplogrupo A difieren por su fecha de origen.
Las mutaciones M91 y P97 distinguen al haplogrupo A del haplogrupo BT . En cromosomas haplogrupo A, el marcador M91 consiste en una secuencia de 8 Base T unidades , mientras que en el haplogrupo BT y en chimpancés cromosomas , este marcador consta de 9 Base T unidades . Esto sugiere que la secuencia 9T del haplogrupo BT era la versión ancestral y que el haplogrupo A se formó mediante la eliminación de una base nucleica .
Pero según Fulvio Cruciani et al. 2011, la región que rodea al marcador M91 es un foco de mutaciones sujetas a mutaciones recurrentes. Por tanto, es posible que la secuencia de 8T del haplogrupo A sea el estado ancestral de M91 y 9T del haplogrupo BT o el estado derivado que apareció por una inserción de 1T. Esto explicaría por qué los subclades A1b y A1a-T, las ramas más antiguas del haplogrupo A, tienen ambos 8T. Además, Cruciani et al. 2011 determinó que el marcador P97, que también se usa para identificar el haplogrupo A, posee el estado ancestral en el haplogrupo A pero el estado derivado en el haplogrupo BT .
Los primeros estudios informaron que los linajes del haplogrupo A surgieron hace unos 60.000 años, que era mucho más reciente que la fecha del ancestro más reciente para los linajes de ADN mitocondrial , cuya fecha de coalescencia , la antigüedad proporcionada por las estadísticas sobre diversidad genética, da entre 150.000 y 200.000 años, lo cual fue algo extraño. Pero Cruciani et al. 2011 retrasó la fecha de la raíz del árbol del cromosoma Y a 142.000 años.
Origen
Varias propuestas sobre el origen del haplogrupo A sugieren que se asoció con la población ancestral de cazadores-recolectores del sur de África , ya que el haplogrupo A es común entre los san . Además, los linajes de ADN mitocondrial más antiguos también están presentes principalmente en la población San. Es más probable que haya un paralelismo evolutivo de mutaciones en las líneas paterna y materna que una divergencia.
Sin embargo, los linajes A del sur de África son subclados de los linajes A basales que se encuentran en otras partes de África. Esto sugiere que los linajes A llegaron al sur de África desde otros lugares. Los dos linajes más antiguos del haplogrupo A, A1b y A1a, se han detectado en África occidental, noroccidental y central. Fulvio Cruciani y col. sugirió que estos linajes pueden haber surgido en algún lugar entre África Central y el Magreb, aunque tal interpretación aún se encuentra en las primeras etapas debido a la cobertura geográfica incompleta de África a partir de los estudios del cromosoma Y.
Distribución
En una muestra compuesta de 3551 hombres africanos , se encontró que el haplogrupo A era del 5,4%. Las frecuencias más altas del haplogrupo A se registran entre los khoisan del sur de África , los falashas y los hablantes de lenguas nilo-saharianas de Sudán y Sudán del Sur .
África central
| África | ||
| . | Población | Frec. (en %) |
| San Tsumkwe ( Namibia ) | 66% | |
| Nama ( Namibia ) | 64 | |
| Dinka ( Sudán del Sur ) | 62 | |
| Shilluk ( Sudán del Sur ) | 53 | |
| Nuba ( Sudán ) | 46 | |
| Khoisan | 44 | |
| Falashas | 41 | |
| Kung / Sekele | ~ 40 | |
| Maba ( Chad ) | 35 | |
| Nuer ( Sudán del Sur ) | 33 | |
| Cuatro ( Sudán ) | 31 | |
| Masai ( Kenia ) | 27 | |
| Nara ( Eritrea ) | 20 | |
| Masalit ( Sudán ) | 19 | |
| Amhara ( Etiopía ) | ~ 16 | |
| Etíopes | 14 | |
| Bantu ( Kenia ) | 14 | |
| Mandara ( Camerún ) | 14 | |
| Hausa ( Sudán ) | 13 | |
| Khwe ( Sudáfrica ) | 12 | |
| Foulbé ( Camerún ) | 12 | |
| Damara ( Namibia ) | 11 | |
| Oromo ( Etiopía ) | 10 | |
| Kunama ( Eritrea ) | 10 | |
| Semita del Sur ( Etiopía ) | 10 | |
| Árabes ( Egipto ) | 3 | |
El haplogrupo A3b2-M13 se observa en poblaciones del norte de Camerún (2/9 = 22% Tupuri , 4/28 = 14% Mandarawa , 2/17 = 12% Foulbé ) y en el este de Congo-Kinshasa (2/9 = 22% para los Alurs , 1/18 = 6% los Hemas , 1/47 = 2% los pigmeos Mbuti ).
El haplogrupo A-M91 (xA1a-M31, A2-M6 / M14 / P3 / P4, A3-M32) (la mutación M91 presente sin ninguna de las mutaciones M31, M6, M14, P3, P4 y M32 presentes) se observa en el Bakolas del sur de Camerún (3/33 = 9%).
Sin haber probado los subclados, el haplogrupo A es observado por muestras en varias poblaciones de Gabón , con 9% (3/33) en los Bakas , 3% (1/36) Ndumus , 2% (1/46) Adoumas , 2% (1/57), Nzebis y 2% (1/60) Tshogos .
este de Africa
El haplogrupo A3b2-M13 es común entre los sudaneses del sur (53%), especialmente entre los [dinka] (16/26 - 61,5%). El haplogrupo A3b2-M13 también se observa en otras poblaciones de Sudán del Sur con una frecuencia del 45% (18/40), incluido 1/40 A3b2a-M171. El haplogrupo A también se informó en el 14,6% (7/48) de Amharas , el 10,3% (8/78) en Oromo , el 13,6% (12/88) en otra población de Etiopía y el 41% entre las Falashas (Cruciani et al. 2002), y también se comparten porcentajes significativos entre los bantú en Kenia (14%, Luis et al.2004 ) y los iraquíes en Tanzania (3/43 = 7, 0% (Luis et al. 2004) a 1/6 = 17% (Knight et al. 2003)).
Africa del Norte
El subclade A1 se observa entre los bereberes de Marruecos, mientras que el subclade A3b2 se observa en aproximadamente el 3% de los hombres egipcios .
Africa del Sur
Un estudio encontró el haplogrupo A en tribus que hablan un idioma khoisan con frecuencias que van del 10% al 70%. Sorprendentemente, el haplogrupo no se encontró entre los hadza de Tanzania, una población tradicionalmente considerada como un vestigio de los khoisan debido a la presencia de clics de consonantes en su idioma.
Eurasia
La forma A1 del haplogrupo A se ha observado en hombres europeos en Inglaterra . Al igual que A3b2, se ha observado con baja frecuencia en Asia Menor , Oriente Medio y algunas islas mediterráneas, entre turcos de las costas del mar Egeo , sardos , palestinos , jordanos , yemeníes y omaníes . Sin haber probado ningún subclade, el haplogrupo A se observa en los griegos de Mitilene en la isla egea de Lesbos y en el sur y centro de Portugal y Madeira. Los autores de un estudio informaron haber encontrado lo que parecía ser el haplogrupo A en el 3,1% (2/65) de los chipriotas , sin descartar definitivamente la posibilidad de que alguno de estos individuos perteneciera a los haplogrupos B o C.
Subclados
A00
| Árbol genealógico del haplogrupo A | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Este árbol filogenético de los subclades del haplogrupo A se basa en el árbol YCC de 2008 y en investigaciones publicadas relacionadas. |
Se lo debemos a Méndez et al. en 2013 el descubrimiento de un haplogrupo hasta ahora desconocido, al que llamaron A00. Aquí está la tabla de estimaciones para la fecha de su inicio:
| Intervalo de confianza del 95% | Promedio | Referencia | Año de publicación |
|---|---|---|---|
| 237 (mínimo) - 581 (máximo) | 338 | Méndez y col. | 2013 |
| 192 - 307 | 254 | Karmin y col. | 2015 |
| 253 - 343 | 291 | Trombetta y col. | 2015 |
| 213 - 293 | 249 | Petr y col. | 2020 |
El intervalo de confianza compatible con todas las publicaciones es de 293 a 253 ka (293.000 a 253.000 años). Sabemos que el Homo sapiens arcaico ya estaba presente alrededor de 300 ka en Jebel Irhoud en Marruecos , sin embargo, la región de identificación de A00 es la de África Central Occidental.
Este haplogrupo hasta ahora desconocido se descubrió en 2012, en el cromosoma Y de un afroamericano llamado Perry que había enviado su ADN para un análisis genealógico comercial. El posterior descubrimiento de otros miembros del haplogrupo A00 llevó a la clasificación del cromosoma Y de Perry como A00a (A-L1149).
La investigación ha demostrado que aproximadamente el 10% de los machos Mbo en el oeste de Camerún pertenecen a un haplogrupo A00b (A-A4987).
Otra investigación realizada en 2015 indica que la población moderna con la tasa más alta de A00 es la de Bangwa , un grupo de cameruneses que hablan yemba , con una tasa de alrededor del 40% de A00a (A-L1149). Además, un hombre de Bangwa no se correspondía ni con A00a ni con A00b.
A2-T- P108
En 2007, siete hombres de Yorkshire en Inglaterra que comparten el apellido fueron identificados como el subgrupo A2-T haplogrupo A. Se descubrió que estos hombres tuvieron un ancestro común en la línea masculina de la XVIII ª siglo, pero ninguna otra información sobre un africano ancestro no fue encontrado. El subgrupo A-P108 es extremadamente raro. Además de los siete machos de Yorkshire , solo otros 25 portadores se encontraron vivos en el subgrupo A-P108, todos de ascendencia africana occidental.
A1b-V164
Se encuentra solo entre los pigmeos de Bakola (sur de Camerún ) en un 8,3% y los bereberes de Argelia en un 1,5%.
A1a-M31
El subclade A1a-M31 se encuentra en aproximadamente 2.8% (8/282) de un conjunto de siete muestras de varios grupos étnicos en Guinea-Bissau , especialmente entre Papel-Manjaco-Mancanha (5/64 = 7.8%). Anteriormente, en un estudio publicado en 2003, Gonçalves et al. informó un 5,1% (14/276) para A1a-M31 en Guinea-Bissau y un 0,5% (1/201) en las islas de Cabo Verde . Los autores de otro estudio informaron 5% (2/39) para A1a-M31 entre los mandingos de Senegambia y 2% (1/55) entre los dogones de Mali . El haplogrupo A1a-M31 también está presente en el 3% (2/64) de los bereberes de Marruecos y el 2,3% (1/44) de una muestra de afiliación étnica no especificada en Malí .
A2-M6
Este subclade del haplogrupo A se encuentra típicamente entre los pueblos Khoisan. Los autores de un estudio informan del haplogrupo A2-M6 (xA2b-P28) (esto significa que excluye su subgrupo A2b-P28 dado por separado) para el 28% (8/29) entre los San Tsumkwe y para el 16% (5/32 ) entre los Kung / Sekele y A2b-P28 para el 17% (5/29) de los San Tsumkwe, el 9% (3/32) de los Kung (personas) / Sekele, el 9% (1/11) de los Namas y el 6% (1/18) de los Damara . En otro estudio, los autores informan de A2 en el 15,4% (6/39) de los hombres Khoisan, incluidos 5/39 A2-M6 / M14 / M23 / M29 / M49 / M71 / M135 / M141 (xA2a-M114) (por lo tanto, el A2 que lleva las 8 mutaciones mencionadas pero sin los portadores M114 dados por separado) y 1/39 A2a-M114.
A3-M32
Este clado contiene las ramas más pobladas del haplogrupo A y se encuentra principalmente en África oriental y meridional .
A3a-M28Este subclade del haplogrupo A3 se observa solo y rara vez en el Cuerno de África . En el 5% (1/20) de una mezcla de hablantes de las lenguas semíticas del sur de Etiopía, el 1,1% (1/88) de los etíopes y el 0,5% (1/201) de los somalíes .
A3b1-M51Este subclade del haplogrupo A3 se encuentra con mayor frecuencia entre los pueblos del grupo Khoisan (6/11 = 55% Nama 11/39 = 28% Khoïsan, 7/32 = 22% Kung / Sekele, 6/29 = 21% San Tsumkwe , 1/18 = 6% Damaras ). Sin embargo, también se encuentra en frecuencias más bajas entre los bantú de Sudáfrica , que comprende 2/28 = 7% sotho- tswana, 3/53 = 6% sudafricanos no khoisan, 4/80 = 5% xhosas y 1/29 = 3% Zulus .
A3b2-M13El subclade del haplogrupo A3 que se encuentra comúnmente en el este de África y el norte de Camerún (A3b2-M13) es diferente de los que se encuentran entre los khoisan y solo está remotamente relacionado con ellos (en realidad no es solo uno de los muchos subclades dentro del haplogrupo A ). Este hallazgo sugiere una vieja discrepancia.
En Sudán , el haplogrupo A3b2-M13 se encuentra en 28/53 = 52,8% de los sudaneses del sur , 13/28 = 46,4% de los nuba en el centro de Sudán, 25/90 = 27,8% de los sudaneses en el oeste , 4/32 = 12,5% De Hausa en Sudán, y 5/216 = 2,3% de Sudán del Norte.
En Etiopía , un estudio informó 14,6% (7/48) para A3b2-M13 en Amharas y 10,3% (8/78) en Oromos . Otro estudio reporta 6.8% (6/88) para A3b2b-M118 y 5.7% (5/88) para A3b2 * -M13 (xA3b2a-M171, A3b2b-M118) entre los etíopes, dando un total de 12, 5% (11 / 88) A3b2-M13.
El haplogrupo A3b2 también se ha observado ocasionalmente fuera de África central y oriental, como en la costa del mar Egeo en Turquía (2/30 = 6,7%), judíos yemeníes (1/20 = 5%), Egipto (4/147 = 2,7%). , 3/92 = 3,3%), árabes palestinos (2/143 = 1,4%), Cerdeña (1/77 = 1,3%, 1/22 = 4, 5%), la capital de Jordania , Ammán (1/101 = 1%) y Omán (1/121 = 0,8%).
Árbol filogenético
Este árbol de subclade del haplogrupo A se basa en el árbol definido por el "Consorcio del Cromosoma Y" (YCC), el "Árbol del Haplogrupo del ADN-Y de ISOGG", y la investigación publicada relacionada con el mismo.
Cromosómico "Adam"
A00 (AF6 / L1284)
- A00a (L1149, FGC25576, FGC26292, FGC26293, FGC27741)
- A00b (A4987 / YP3666, A4981, A4982 / YP2683, A4984 / YP2995, A4985 / YP3292, A4986, A4988 / YP3731)
A0-T (L1085)
- A0 (CTS2809 / L991) ex-A1b
-
A1 (P305) ex-A1a-T, A0 y A1b
- A1a (M31)
-
A1b (P108) ex-A2-T
-
A1b1 (L419 / PF712)
-
A1b1a (L602, V50, V82, V198, V224)
-
A1b1a1 (M14) ex A2
-
A1b1a1a (M6)
- A1b1a1a1 (P28) ex-A1b1a1a1b y A2b
-
A1b1a1a (M6)
-
A1b1a1 (M14) ex A2
-
A1b1b (M32) ex-A3
- A1b1b1 (M28) ex-A3a
-
A1b1b2 (L427)
-
A1b1b2a (M51 / Página 42) ex-A3b1
- A1b1b2a1 (P291)
-
A1b1b2b (M13 / PF1374) ex-A3b2
- A1b1b2b1 (M118)
-
A1b1b2a (M51 / Página 42) ex-A3b1
-
A1b1a (L602, V50, V82, V198, V224)
- BT (M91)
-
A1b1 (L419 / PF712)
Notas y referencias
Notas
- Las otras mutaciones son: M49, M71, M135, M141, M196, M206, M212, MEH1, P3, P4, P5, P36.1, PK1, P247 y P248
Referencias
- (en) Fulvio Cruciani et al. , “ Una raíz revisada para el árbol filogenético cromosómico Y humano: el origen de la diversidad patrilineal en África ” , The American Journal of Human Genetics , vol. 88, n o 6,19 de mayo de 2011( DOI 10.1016 / j.ajhg.2011.05.002 , leer en línea , consultado el 1 er de abril de 2012 )
- Karmin y col. , " Un cuello de botella reciente de la diversidad del cromosoma Y coincide con un cambio global en la cultura ", Genome Research , vol. 25, n o 4,2015, p. 459–66 ( PMID 25770088 , PMCID 4381518 , DOI 10.1101 / gr.186684.114 )
- L. Mendez et al. , " La divergencia de los cromosomas Y humanos modernos y neandertales ", The American Journal of Human Genetics , vol. 98, n o 4,2016, p. 728–34 ( PMID 27058445 , PMCID 4833433 , DOI 10.1016 / j.ajhg.2016.02.023 )
- (en) Khaled K. Abu-Amero et al. , “ La diversidad del cromosoma Y de Arabia Saudita y su relación con las regiones cercanas ” , BMC Genetics , vol. 10, n o 59,2009( PMID 19772609 , DOI 10.1186 / 1471-2156-10-59 , leer en línea )
- (en) " Y-DNA haplogrupo árbol " , Sociedad Internacional de Genética Genealogía,3 de febrero de 2010(consultado el 17 de diciembre de 2010 )
- (en) Gemma Berniell-Lee , Francesc Calafell , Elena Bosch et al. , “ Implicaciones genéticas y demográficas de la expansión bantú: conocimientos de los linajes paternos humanos ” , Biología molecular y evolución , vol. 26, n o 7,26 de julio de 2010, p. 1581-1589 ( PMID 19369595 , DOI 10.1093 / molbev / msp069 , leer en línea [EPUB] , consultado el 30 de noviembre de 2010 )
- (en) Alexandra Rosa , Carolina Ornelas , Mark A Jobling et al. , “La diversidad del cromosoma Y en la población de Guinea-Bissau: una perspectiva multiétnica ” , BMC Evolutionary Biology , vol. 2007, n o 7,2007, p. 124 ( PMID 17662131 , PMCID 1976131 , DOI 10.1186 / 1471-2148-7-124 )
- , cf. Apéndice A: Frecuencias de haplotipos del cromosoma Y
- (en) PA Underhill , G. Passarino AA Lin et al. , “ La filogeografía de los haplotipos binarios del cromosoma Y y los orígenes de las poblaciones humanas modernas ” , Annals of Human Genetics , vol. 65, n o 1,Enero de 2001, p. 43–62 ( PMID 11415522 , DOI 10.1046 / j.1469-1809.2001.6510043.x )
- (en) TM Karafet , FL Méndez , MB Meilerman , PA Underhill , SL Zegura y MF Hammer , “ Nuevos polimorfismos binarios remodelar y aumentar la resolución de la Y haplogrupo árbol cromosómica humana ” , Genome Research , vol. 18, n o 5,2008, p. 830–8 ( PMID 18385274 , PMCID 2336805 , DOI 10.1101 / gr.7172008 , leer en línea )
- (en) Batini et al. , “ Firmas de los procesos de población preagrícola en África subsahariana según lo revelado por la filogeografía de los primeros linajes del cromosoma Y ” , Biología Molecular y Evolución ,2011( DOI 10.1093 / molbev / msr089 , leer en línea , consultado el 1 er de abril de 2012 )
- (en) TE Rey , EJ Parkin , G Swinfield et al. , “¿ Africanos en Yorkshire? El clado más arraigado de la filogenia Y dentro de una genealogía inglesa ” , Eur. J. Hum. Escoba. , vol. 15, n o 3,Marzo de 2007, p. 288–93 ( PMID 17245408 , PMCID 2590664 , DOI 10.1038 / sj.ejhg.5201771 )
- 28/53 (Dinka, Nuer y Shilluk), (en) HY Hassan , PA Underhill , LL Cavalli-Sforza y ME Ibrahim , “ Variación del cromosoma Y entre los sudaneses: restringida flujo de genes, concordancia con el lenguaje, la geografía y la historia ” , Am. J. Phys. Anthropol. , vol. 137, n o 3,Noviembre de 2008, p. 316–23 ( PMID 18618658 , DOI 10.1002 / ajpa.20876 , leer en línea )
- (en) PA Underhill , P Shen , Lin et al. , “ Variación de la secuencia del cromosoma Y e historia de las poblaciones humanas ” , Nat. Escoba. , vol. 26, n o 3,noviembre 2000, p. 358–61 ( PMID 11062480 , DOI 10.1038 / 81685 )
- (en) Fulvio Cruciani , Piero Santolamazza , Peidong Shen et al. , " Una migración hacia atrás de Asia al África subsahariana está respaldada por un análisis de alta resolución de los haplotipos del cromosoma Y humano " , American Journal of Human Genetics , vol. 70, n os 1197 a 1214,2002
- (en) Peidong Shen , Tal Lavi Toomas Kivisild et al. , “ Reconstrucción de patrilinajes y matrilinajes de samaritanos y otras poblaciones israelíes a partir del cromosoma Y y la variación de la secuencia del ADN mitocondrial ” , Mutación humana , n o 242004, p. 248-260
- (en) Fulvio Cruciani , Beniamino Trombetta , Daniele Sellitto et al. , “ Haplogrupo del cromosoma Y humano R-V88: un registro genético paterno de las conexiones transsaharianas del Holoceno medio temprano y la propagación de las lenguas chadic ” , European Journal of Human Genetics ,2010, p. 1-8
- (en) O Semino , AS Santachiara-Benerecetti , F Falaschi , LL Cavalli-Sforza y PA Underhill , “Los etíopes y los khoisan comparten los clados más profundos de la filogenia del cromosoma Y humano ” , Am. J. Mmm. Escoba. , vol. 70, n o 1,enero 2002, p. 265–8 ( PMID 11719903 , PMCID 384897 , DOI 10.1086 / 338306 , leer en línea )
- (en) JR Luis , DJ Rowold , M. Regueiro et al. , “ El Levante versus el Cuerno de África: evidencia de corredores bidireccionales de las migraciones humanas ” , American Journal of Human Genetics , vol. 74, núms . 532–544,2004
- (en) F. Di Giacomo , F. Luca , N. Anagnou et al. , “Los patrones clinales de la diversidad cromosómica Y humana en la Italia continental y Grecia están dominados por efectos de derivación y fundador ” , Molecular Phylogenetics and Evolution , vol. 28, n o 3,2003, p. 387–395 ( PMID 12927125 , DOI 10.1016 / S1055-7903 (03) 00016-2 )
- (en) Rita Gonçalves , Ana Freitas , Marta Branco et al. , “ Los linajes del cromosoma Y de Portugal, Madeira y Açores registran elementos de ascendencia sefardí y bereber ” , Annals of Human Genetics , vol. 69, n o Pt 4,2005, p. 443–454 ( PMID 15996172 , DOI 10.1111 / j.1529-8817.2005.00161.x )
- (en) C. Capelli , N. Redhead , V. Romano et al. , " Estructura de la población en la cuenca del Mediterráneo: perspectiva del cromosoma AY " , Annals of Human Genetics ,2005
- grupo = "N"> Las otras mutaciones son: P100, P291
- grupo = "N"> Las otras mutaciones son: M63, M127, M202, M219, M305
- group = "N"> Las otras mutaciones son: M190, M220 y P289
- Fernando Méndez , Thomas Krahn , Bonnie Schrack , Astrid-Maria Krahn , Krishna Veeramah , agosto de Woerner , Forka Leypey Mathew Fomine , Neil Bradman , Mark Thomas , Tatiana M. Karafet y Michael F. Hammer , “ paterna Un afroamericano linaje añade una raíz extremadamente antigua al árbol filogenético del cromosoma Y humano ”, American Journal of Human Genetics , vol. 92, n o 3,2013, p. 454–9 ( PMID 23453668 , PMCID 3591855 , DOI 10.1016 / j.ajhg.2013.02.002 , leer en línea ).
- M. Karmin , Saag , Vicente y Wilson Sayres , " Un cuello de botella reciente de la diversidad del cromosoma Y coincide con un cambio global en la cultura ", Genome Research , vol. 25, n o 4,2015, p. 459–66 ( PMID 25770088 , PMCID 4381518 , DOI 10.1101 / gr.186684.114 ).
- B. Trombetta , D'Atanasio , Massaia , Myres , Scozzari , Cruciani y Novelletto , “ Diferencias regionales en la acumulación de SNP en la porción masculina específica de los patrones autosómicos replicados del cromosoma Y humano: implicaciones para la datación genética ”, PLOS ONE , vol. 10, n o 7,2015, e0134646 ( PMID 26226630 , PMCID 4520482 , DOI 10.1371 / journal.pone.0134646 , Bibcode 2015PLoSO..1034646T ).
- Martin Petr, Mateja Hajdinjak, Qiaomei Fu, Elena Essel, Hélène Rougier, Isabelle Crevecoeur, Patrick Semal, Liubov V.Golovanova, Vladimir B. Doronichev, Carles Lalueza-Fox, Marco de la Rasilla, Antonio Rosas, Michael V.Shunkov, Maxim B. Kozlikin, Anatoli P. Derevianko, Benjamin Vernot, Matthias Meyer, Janet Kelso, " La historia evolutiva de los cromosomas Y de Neanderthal y Denisovan " , Science , volumen 369, número 6511, páginas 1653-16562020.
- Descendiente de Albert Perry, un esclavo nacido en los Estados Unidos entre 1819-1827, que vive en el condado de York, Carolina del Sur. Ver FamilyTreeDNA, gráfico de haplogrupo A
- ¿Cuáles de los pueblos de Camerún tienen miembros del haplogrupo A00? // experiment.com actualización de la investigación financiada (Schrack / Fomine Forka) disponible en línea Citas: Ahora podemos ver claramente que con un 40% de A00, los Bangwa representan el epicentro de A00 en esta región y muy posiblemente en el mundo. Como compartí en la última nota de laboratorio, encontramos que hasta ahora hay dos subgrupos principales de A00, definidos por diferentes mutaciones Y-SNP, que, naturalmente, se dividen a lo largo de líneas étnicas: A00a entre los Bangwa y A00b entre los Mbo. También encontramos la única muestra de Bangwa que no pertenecía a ninguno de los subgrupos ".
- Artículo de periódico: (en) " Clan de Yorkshire vinculado a África " , en BBC News ,24 de enero de 2007(consultado el 1 er de abril de 2012 )
- Rita Gonçalves , Alexandra Rosa , Ana Freitas et al. " Los linajes del cromosoma Y en las islas de Cabo Verde son testigos del origen geográfico diverso de los primeros pobladores masculinos de las tic ", Human Genetics , n o 1132003, p. 467-472
- (en) HY Hassan , PA Underhill , LL Cavalli-Sforza y ME Ibrahim , " Variación del cromosoma Y entre los sudaneses: flujo genético restringido, consistente con el idioma, la geografía y la historia " , Am J Phys .. Anthropol. , vol. 137, n o 3,Noviembre de 2008, p. 316–23 ( PMID 18618658 , DOI 10.1002 / ajpa.20876 , leer en línea ). El grupo de "Sudán del Sur" incluye 26 Dinka, 15 Shilluks y 12 Nuers. El grupo de los "sudaneses occidentales" incluye 26 Borgus, 32 Masalits y 32 Hornos. El grupo de "sudaneses del norte" incluye 39 nubios, 42 bejas, 33 coptos, 50 gaales, 28 meserias y 24 arakis.
- (en) Cengiz Cinnioglu Roy King Toomas Kivisild et al. , “ Excavación de estratos de haplotipos del cromosoma Y en Anatolia ” , Human Genetics , vol. 114,2004, p. 127–148 ( DOI 10.1007 / s00439-003-1031-4 )
- (en) Almut Nebel , Dvora Vein , Bernd Brinkmann et al. , " La reserva del cromosoma Y de los judíos como parte del panorama genético del Medio Oriente " , American Journal of Human Genetics , vol. 69,2001, p. 1095-1112
- (en) Ornella Semino , Giuseppe Passarino , Peter J. Oefner et al. , “ El legado genético del Homo sapiens sapiens paleolítico en los europeos existentes: perspectiva cromosómica AY ” , Science , vol. 290,10 de noviembre de 2000
- (en) C Flores , N Maca-Meyer , JM Larruga , VM Cabrera , N Karadsheh y AM Gonzalez , " Aislados en un corredor de migración: un análisis de alta resolución de la variación del cromosoma Y en Jordania " , J. Hum. Escoba. , vol. 50, n o 9,2005, p. 435–441 ( PMID 16142507 , DOI 10.1007 / s10038-005-0274-4 )
- (en) Thomas Krahn , " YCC Tree " , Houston, Texas, FTDNA (consultado el 16 de mayo de 2011 )
Apéndices
Artículos relacionados
|
Haplogrupos del cromosoma Y (ADN-Y) | ||||||||||||||||||||||||
| Antepasado patrilineal común más reciente | ||||||||||||||||||||||||
| A | ||||||||||||||||||||||||
| BT | ||||||||||||||||||||||||
| B | Connecticut | |||||||||||||||||||||||
| DE | CF | |||||||||||||||||||||||
| D | mi | VS | F | |||||||||||||||||||||
| GRAMO | H | IJK | ||||||||||||||||||||||
| IJ | K | |||||||||||||||||||||||
| I | J | LT | K2 | |||||||||||||||||||||
| I1 | L | T | SRA | PAG | NO | |||||||||||||||||||
| METRO | S | Q | R | NO | O | |||||||||||||||||||
| R1 | R2 | |||||||||||||||||||||||
| R1a | R1b | |||||||||||||||||||||||
- General:
-
Genética del cromosoma Y :
- Tabla de conversión de haplogrupos del cromosoma Y
enlaces externos
- (es) Proyecto de haplogrupo africano en el sitio web de FamilyTreeDNA
- (en) Haplogrupo A en el sitio web de National Geographic